一篇很好的介绍RNAi实验原理与方法的文章,希望对您有所帮助
丁香园论坛
2322
RNAi实验原理与方法
近年来的研究表明,将与mRNA对应的正义RNA和反义RNA组成的双链RNA(dsRNA)导入细胞,可以使mRNA发生特异性的降解,导致其相应的基因沉默。这种转录后基因沉默机制(post-transcriptional gene silencing, PTGS)被称为RNA干扰(RNAi)。
一、RNAi的分子机制
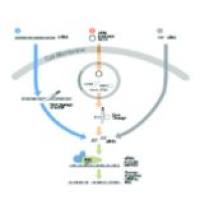
通过生化和遗传学研究表明,RNA干扰包括起始阶段和效应阶段(inititation and effector steps)。在起始阶段,加入的小分子RNA被切割为21-23核苷酸长的小分子干扰RNA片段(small interfering RNAs, siRNAs)。证据表明;一个称为Dicer的酶,是RNase III家族中特异识别双链RNA的一员,它能以一种ATP依赖的方式逐步切割由外源导入或者由转基因,病毒感染等各种方式引入的双链RNA,切割将RNA降解为19-21bp的双链RNAs(siRNAs),每个片段的3’端都有2个碱基突出。
在RNAi效应阶段,siRNA双链结合一个核酶复合物从而形成所谓RNA诱导沉默复合物(RNA-induced silencing complex, RISC)。激活RISC需要一个ATP依赖的将小分子RNA解双链的过程。激活的RISC通过碱基配对定位到同源mRNA转录本上,并在距离siRNA3’端12个碱基的位置切割mRNA。尽管切割的确切机制尚不明了,但每个RISC都包含一个siRNA和一个不同于Dicer的RNA酶。
另外,还有研究证明含有启动子区的dsRNA在植物体内同样被切割成21-23nt长的片段,这种dsRNA可使内源相应的DNA序列甲基化,从而使启动子失去功能,使其下游基因沉默.
二、如何进行RNAi试验
(一)siRNA的设计
1. 在设计RNAi实验时,可以先在以下网站进行目标序列的筛选:
http://www.genesil.com/business/products/order2.htm
http://www.ambion.com/techlib/misc/siRNA_finder.html
http://www.ic.sunysb.edu/Stu/shilin/rnai.html
http://design.dharmacon.com/rnadesign/default.aspx?SID=45358710
2.RNAi目标序列的选取原则:
(1)从转录本(mRNA)的AUG起始密码开始,寻找“AA”二连序列,并记下其3'端的19个碱基序列,作为潜在的siRNA靶位点。有研究结果显示GC含量在45%—55%左右的siRNA要比那些GC含量偏高的更为有效。
Tuschl等建议在设计siRNA时不要针对5'和3'端的非编码区(untranslated regions,UTRs),原因是这些地方有丰富的调控蛋白结合区域,而这些UTR结合蛋白或者翻译起始复合物可能会影响siRNP核酸内切酶复合物结合mRNA从而影响siRNA的效果。
(2)将潜在的序列和相应的基因组数据库(人,或者小鼠,大鼠等等)进行比较,排除那些和其他编码序列/EST同源的序列。
例如使用BLAST( www.ncbi.nlm.nih.gov/BLAST/)
(3)选出合适的目标序列进行合成。通常一个基因需要设计多个靶序列的siRNA,以找到最有效的siRNA序列。
3.阴性对照
一个完整的siRNA实验应该有阴性对照,作为阴性对照的siRNA应该和选中的siRNA序列有相同的组成,但是和mRNA没有明显的同源性。通常的做法是将选中的siRNA序列打乱,同样要检查结果以保证它和目的靶细胞中其他基因没有同源性。
4.目前已证实的siRNA可以在下面的网页找到:
http://design.dharmacon.com/catalog/category.aspx?key=49
http://www.ambion.com/techlib/tb/tb_502.html
http://web.mit.edu/mmcmanus/www/siRNADB.html
http://python.penguindreams.net/Order_Entry/jsp/BrowseCatalog.jsp?Category=Published
(二)siRNA的制备
目前为止较为常用的方法有通过化学合成,体外转录,长片断dsRNAs经RNase III 类降解 (e.g. Dicer, E. coli, RNase III)体外制备siRNA,以及通过siRNA表达载体或者病毒载体,PCR制备的siRNA表达框在细胞中表达产生siRNA。
体外制备
1.化学合成
许多国外公司都可以根据用户要求提供高质量的化学合成siRNA。主要的缺点包括价格高,定制周期长,特别是有特殊需求的。由于价格比其他方法高,为一个基因合成3—4对siRNAs 的成本就更高了,比较常见的做法是用其他方法筛选出最有效的序列再进行化学合成。
最适用于:已经找到最有效的siRNA的情况下,需要大量siRNA进行研究
不适用于:筛选siRNA等长时间的研究,主要原因是价格因素
2.体外转录
以DNA Oligo为模版,通过体外转录合成siRNAs,成本相对化学合成法而言比较低,而且能够比化学合成法更快的得到siRNAs。不足之处是实验的规模受到限制,虽然一次体外转录合成能提供足够做数百次转染的siRNAs,但是反应规模和量始终有一定的限制。而且和化学合成相比,还是需要占用研究人员相当的时间。值得一提的是体外转录得到的siRNAs毒性小,稳定性好,效率高,只需要化学合成的siRNA量的1/10就可以达到化学合成siRNA所能达到的效果,从而使转染效率更高。
最适用于:筛选siRNAs,特别是需要制备多种siRNAs,化学合成的价格成为障碍时。
不适用于:实验需要大量的,一个特定的siRNA。长期研究。
3.用RNase III 消化长片断双链RNA制备siRNA
其他制备siRNA的方法的缺陷是需要设计和检验多个siRNA序列以便找到一个有效的siRNA。而用这种方法——制备一份混合有各种siRNAs “混合鸡尾酒” 就可以避免这个缺陷。选择通常是200—1000碱基的靶mRNA模版,用体外转录的方法制备长片断双链dsRNA ,然后用RNase III (or Dicer) 在体外消化,得到一种siRNAs“混合鸡尾酒”。在除掉没有被消化的dsRNA后,这个siRNA混合物就可以直接转染细胞,方法和单一的siRNA转染一样。由于siRNA混合物中有许多不同的siRNAs,通常能够保证目的基因被有效地抑制。
dsRNA消化法的主要优点在于可以跳过检测和筛选有效siRNA序列的步骤,为研究人员节省时间和金钱(注意:通常用RNAse III通常比用Dicer要便宜)。不过这种方法的缺点也很明显,就是有可能引发非特异的基因沉默,特别是同源或者是密切相关的基因。现在多数的研究显示这种情况通常不会造成影响。
最适用于:快速而经济地研究某个基因功能缺失的表型
不适用于:长时间的研究项目,或者是需要一个特定的siRNA进行研究,特别是基因治疗
体内表达
前面的3种方法主要都是体外制备siRNAs,并且需要专门的RNA转染试剂将siRNAs转到细胞内。而采用siRNA表达载体和基于PCR的表达框架则属于:从转染到细胞的DNA模版中在体内转录得到siRNAs。这两种方法的优点在于不需要直接操作RNA。
4. siRNA表达载体
多数的siRNA表达载体依赖三种RNA聚合酶III 启动子(pol III)中的一种,操纵一段小的发夹RNA(short hairpin RNA, shRNA)在哺乳动物细胞中的表达。这三类启动子包括大家熟悉的人源和鼠源的U6启动子和人H1启动子。之所以采用RNA pol III启动子是由于它可以在哺乳动物细胞中表达更多的小分子RNA,而且它是通过添加一串(3到6个)U来终止转录的。要使用这类载体,需要订购2段编码短发夹RNA序列的DNA单链,退火,克隆到相应载体的pol III 启动子下游。由于涉及到克隆,这个过程需要几周甚至数月的时间,同时也需要经过测序以保证克隆的序列是正确的。
siRNA表达载体的优点在于可以进行较长期研究——带有抗生素标记的载体可以在细胞中持续抑制靶基因的表达,持续数星期甚至更久。
病毒载体也可用于siRNA表达,其优势在于可以直接高效率感染细胞进行基因沉默的研究,避免由于质粒转染效率低而带来的种种不便,而且转染效果更加稳定。
最适用于:已知一个有效的siRNA序列,需要维持较长时间的基因沉默。
不适用于:筛选siRNA序列(其实主要是指需要多个克隆和测序等较为费时、繁琐的工作)。
5. siRNA表达框架
siRNA表达框架(siRNA expression cassettes,SECs)是一种由PCR得到的siRNA表达模版,包括一个RNA pol III启动子,一段发夹结构siRNA,一个RNA pol III终止位点,能够直接导入细胞进行表达而无需事前克隆到载体中。和siRNA表达载体不同的是,SECs不需要载体克隆、测序等颇为费时的步骤,可以直接由PCR得到,不用一天的时间。因此,SECs成为筛选siRNA的最有效工具,甚至可以用来筛选在特定的研究体系中启动子和siRNA的最适搭配。如果在PCR两端添加酶切位点,那么通过SECs筛选出的最有效的siRNA后,可以直接克隆到载体中构建siRNA表达载体。构建好的载体可以用于稳定表达siRNA和长效抑制的研究。
这个方法的主要缺点是①PCR产物很难转染到细胞中(晶赛公司的Protocol可以解决这一问题)②不能进行序列测定,PCR和DNA合成时可能差生的误读不能被发现导致结果不理想。
最适用于:筛选siRNA序列,在克隆到载体前筛选最佳启动子
不适用于:长期抑制研究。(如果克隆到载体后就可以了)
(三)siRNA的转染
将制备好的siRNA,siRNA表达载体或表达框架转导至真核细胞中的方法主要有以下几种:
1.磷酸钙共沉淀
将氯化钙,RNA(或DNA)和磷酸缓冲液混合,沉淀形成包含DNA且极小的不溶的磷酸钙颗粒。磷酸钙-DNA复合物粘附到细胞膜并通过胞饮进入目的细胞的细胞质。沉淀物的大小和质量对于磷酸钙转染的成功至关重要。在实验中使用的每种试剂都必须小心校准,保证质量,因为甚至偏离最优条件十分之一个pH都会导致磷酸钙转染的失败。
2.电穿孔法
电穿孔通过将细胞暴露在短暂的高场强电脉冲中转导分子。将细胞悬浮液置于电场中会诱导沿细胞膜的电压差异,据认为这种电压差异会导致细胞膜暂时穿孔。电脉冲和场强的优化对于成功的转染非常重要,因为过高的场强和过长的电脉冲时间会不可逆地伤害细胞膜而裂解细胞。一般,成功的电穿孔过程都伴随高水平(50%或更高)的毒性。
3.DEAE-葡聚糖和polybrene
带正电的DEAE-葡聚糖或polybrene多聚体复合物和带负电的DNA分子使得DNA可以结合在细胞表面。通过使用DMSO或甘油获得的渗透休克将DNA复合体导入。两种试剂都已成功用于转染。DEAE-葡聚糖仅限于瞬时转染。
4.机械法
转染技术也包括使用机械的方法,比如显微注射和基因枪(biolistic particle)。显微注射使用一根细针头将DNA,RNA或蛋白直接转入细胞质或细胞核。基因枪使用高压microprojectile将大分子导入细胞。
5.阳离子脂质体试剂
在优化条件下将阳离子脂质体试剂加入水中时,其可以形成微小的(平均大小约100-400nm)单层脂质体。这些脂质体带正电,可以靠静电作用结合到DNA的磷酸骨架上以及带负电的细胞膜表面。因此使用阳离子脂质体转染的原理与以前利用中性脂质体转染的原理不同。使用阳离子脂质体试剂,DNA并没有预先包埋在脂质体中,而是带负电的DNA自动结合到带正电的脂质体上,形成DNA-阳离子脂质体复合物。据称,一个约5kb的质粒会结合2-4个脂质体。被俘获的DNA就会被导入培养的细胞。现存对DNA转导原理的证据来源于内吞体和溶酶体。
为了达到高的转染效率,在转染实验过程中,需要注意以下几点:
1.纯化siRNA
在转染前要确认siRNA的大小和纯度。为得到高纯度的siRNA,推荐用玻璃纤维结合,洗脱或通过15-20%丙烯酰胺胶除去反应中多余的核苷酸,小的寡核苷酸,蛋白和盐离子。注意:化学合成的RNA通常需要跑胶电泳纯化(即PAGE胶纯化)。
2.避免RNA酶污染
微量的RNA酶将导致siRNA实验失败。由于实验环境中RNA酶普遍存在,如皮肤,头发,所有徒手接触过的物品或暴露在空气中的物品等,此保证实验每个步骤不受RNA酶污染非常重要。
3.健康的细胞培养物和严格的操作确保转染的重复性
通常,健康的细胞转染效率较高。此外,较低的传代数能确保每次实验所用细胞的稳定性。为了优化实验,推荐用50代以下的转染细胞,否则细胞转染效率会随时间明显下降。
4.避免使用抗生素
Ambion公司推荐从细胞种植到转染后72小时期间避免使用抗生素。抗生素会在穿透的细胞中积累毒素。有些细胞和转染试剂在siRNA转染时需要无血清的条件。这种情况下,可同时用正常培养基和无血清培养基做对比实验,以得到最佳转染效果。
5.选择合适的转染试剂
针对siRNA制备方法以及靶细胞类型的不同,选择好的转染试剂和优化的操作对siRNA实验的成功至关重要。
6.通过合适的阳性对照优化转染和检测条件
对大多数细胞,看家基因是较好的阳性对照。将不同浓度的阳性对照的siRNA转入靶细胞(同样适合实验靶siRNA),转染48小时后统计对照蛋白或mRNA相对于未转染细胞的降低水平。过多的siRNA将导致细胞毒性以至死亡。
7.通过标记siRNA来优化实验
荧光标记的siRNA能用来分析siRNA稳定性和转染效率。标记的siRNA还可用作siRNA胞内定位及双标记实验(配合标记抗体)来追踪转染过程中导入了siRNA的细胞,将转染与靶蛋白表达的下调结合起来。
三、RNAi的应用前景
1. 研究基因功能的新工具
已有研究表明RNAi能够在哺乳动物中灭活或降低特异性基因的表达,制作多种表型,而且抑制基因表达的时间可以随意控制在发育的任何阶段,产生类似基因敲除的效应。线虫和果蝇的全部基因组序列已测试完毕,发现大量未知功能的新基因,RNAi将大大促进对这些新基因功能的研究。与传统的基因敲除技术相比,这一技术具有投入少,周期短,操作简单等优势,近来RNAi成功用于构建转基因动物模型的报道日益增多,标志着RNAi将成为研究基因功能不可或缺的工具。
2. 研究信号传导通路的新途径
联合利用传统的缺失突变技术和RNAi技术可以很容易地确定复杂的信号传导途径中不同基因的上下游关系,Clemensy等应用RNAi研究了果蝇细胞系中胰岛素信息传导途径,取得了与已知胰岛素信息传导通路完全一致的结果,在此基础上分析了DSH3PX1与DACK之间的关系, 证实了DACK是位于DSH3PX1磷酸化的上游激酶. RNAi技术较传统的转染实验简单、快速、重复性好,克服了转
染实验中重组蛋白特异性聚集和转染效率不高的缺点, 因此认为RNAi技术将可能成为研究细胞信号传导通路的新途径。
3.开展基因治疗的新策略
RNAi具有抵抗病毒入侵,抑制转座子活动,防止自私基因序列过量增殖等作用,因此可以利用RNAi现象产生抗病毒的植物和动物,并可利用不同病毒转录序列中高度同源区段相应的dsRNA抵抗多种病毒。
肿瘤是多个基因相互作用的基因网络调控的结果,传统技术诱发的单一癌基因的阻断不可能完全抑制或逆转肿瘤的生长, 而RNAi可以利用同一基因家族的多个基因具有一段同源性很高的保守序列这一特性, 设计针对这一区段序列的dsRNA分子,只注射一种dsRNA即可以产生多个基因同时剔除的表现,也可以同时注射多种dsRNA而将多个序列不相关的基因同时剔除。
尽管目前RNAi技术在哺乳动物中的应用还处于探索阶段,但它在斑马鱼和老鼠等脊椎动物中的成功应用预示着RNAi将成为基因治疗中重要的组成部分,人工合成的dsRNA寡聚药物的开发将可能成为极具发展前途的新兴产业。
近年来的研究表明,将与mRNA对应的正义RNA和反义RNA组成的双链RNA(dsRNA)导入细胞,可以使mRNA发生特异性的降解,导致其相应的基因沉默。这种转录后基因沉默机制(post-transcriptional gene silencing, PTGS)被称为RNA干扰(RNAi)。
一、RNAi的分子机制
通过生化和遗传学研究表明,RNA干扰包括起始阶段和效应阶段(inititation and effector steps)。在起始阶段,加入的小分子RNA被切割为21-23核苷酸长的小分子干扰RNA片段(small interfering RNAs, siRNAs)。证据表明;一个称为Dicer的酶,是RNase III家族中特异识别双链RNA的一员,它能以一种ATP依赖的方式逐步切割由外源导入或者由转基因,病毒感染等各种方式引入的双链RNA,切割将RNA降解为19-21bp的双链RNAs(siRNAs),每个片段的3’端都有2个碱基突出。
在RNAi效应阶段,siRNA双链结合一个核酶复合物从而形成所谓RNA诱导沉默复合物(RNA-induced silencing complex, RISC)。激活RISC需要一个ATP依赖的将小分子RNA解双链的过程。激活的RISC通过碱基配对定位到同源mRNA转录本上,并在距离siRNA3’端12个碱基的位置切割mRNA。尽管切割的确切机制尚不明了,但每个RISC都包含一个siRNA和一个不同于Dicer的RNA酶。
另外,还有研究证明含有启动子区的dsRNA在植物体内同样被切割成21-23nt长的片段,这种dsRNA可使内源相应的DNA序列甲基化,从而使启动子失去功能,使其下游基因沉默.
二、如何进行RNAi试验
(一)siRNA的设计
1. 在设计RNAi实验时,可以先在以下网站进行目标序列的筛选:
http://www.genesil.com/business/products/order2.htm
http://www.ambion.com/techlib/misc/siRNA_finder.html
http://www.ic.sunysb.edu/Stu/shilin/rnai.html
http://design.dharmacon.com/rnadesign/default.aspx?SID=45358710
2.RNAi目标序列的选取原则:
(1)从转录本(mRNA)的AUG起始密码开始,寻找“AA”二连序列,并记下其3'端的19个碱基序列,作为潜在的siRNA靶位点。有研究结果显示GC含量在45%—55%左右的siRNA要比那些GC含量偏高的更为有效。
Tuschl等建议在设计siRNA时不要针对5'和3'端的非编码区(untranslated regions,UTRs),原因是这些地方有丰富的调控蛋白结合区域,而这些UTR结合蛋白或者翻译起始复合物可能会影响siRNP核酸内切酶复合物结合mRNA从而影响siRNA的效果。
(2)将潜在的序列和相应的基因组数据库(人,或者小鼠,大鼠等等)进行比较,排除那些和其他编码序列/EST同源的序列。
例如使用BLAST( www.ncbi.nlm.nih.gov/BLAST/)
(3)选出合适的目标序列进行合成。通常一个基因需要设计多个靶序列的siRNA,以找到最有效的siRNA序列。
3.阴性对照
一个完整的siRNA实验应该有阴性对照,作为阴性对照的siRNA应该和选中的siRNA序列有相同的组成,但是和mRNA没有明显的同源性。通常的做法是将选中的siRNA序列打乱,同样要检查结果以保证它和目的靶细胞中其他基因没有同源性。
4.目前已证实的siRNA可以在下面的网页找到:
http://design.dharmacon.com/catalog/category.aspx?key=49
http://www.ambion.com/techlib/tb/tb_502.html
http://web.mit.edu/mmcmanus/www/siRNADB.html
http://python.penguindreams.net/Order_Entry/jsp/BrowseCatalog.jsp?Category=Published
(二)siRNA的制备
目前为止较为常用的方法有通过化学合成,体外转录,长片断dsRNAs经RNase III 类降解 (e.g. Dicer, E. coli, RNase III)体外制备siRNA,以及通过siRNA表达载体或者病毒载体,PCR制备的siRNA表达框在细胞中表达产生siRNA。
体外制备
1.化学合成
许多国外公司都可以根据用户要求提供高质量的化学合成siRNA。主要的缺点包括价格高,定制周期长,特别是有特殊需求的。由于价格比其他方法高,为一个基因合成3—4对siRNAs 的成本就更高了,比较常见的做法是用其他方法筛选出最有效的序列再进行化学合成。
最适用于:已经找到最有效的siRNA的情况下,需要大量siRNA进行研究
不适用于:筛选siRNA等长时间的研究,主要原因是价格因素
2.体外转录
以DNA Oligo为模版,通过体外转录合成siRNAs,成本相对化学合成法而言比较低,而且能够比化学合成法更快的得到siRNAs。不足之处是实验的规模受到限制,虽然一次体外转录合成能提供足够做数百次转染的siRNAs,但是反应规模和量始终有一定的限制。而且和化学合成相比,还是需要占用研究人员相当的时间。值得一提的是体外转录得到的siRNAs毒性小,稳定性好,效率高,只需要化学合成的siRNA量的1/10就可以达到化学合成siRNA所能达到的效果,从而使转染效率更高。
最适用于:筛选siRNAs,特别是需要制备多种siRNAs,化学合成的价格成为障碍时。
不适用于:实验需要大量的,一个特定的siRNA。长期研究。
3.用RNase III 消化长片断双链RNA制备siRNA
其他制备siRNA的方法的缺陷是需要设计和检验多个siRNA序列以便找到一个有效的siRNA。而用这种方法——制备一份混合有各种siRNAs “混合鸡尾酒” 就可以避免这个缺陷。选择通常是200—1000碱基的靶mRNA模版,用体外转录的方法制备长片断双链dsRNA ,然后用RNase III (or Dicer) 在体外消化,得到一种siRNAs“混合鸡尾酒”。在除掉没有被消化的dsRNA后,这个siRNA混合物就可以直接转染细胞,方法和单一的siRNA转染一样。由于siRNA混合物中有许多不同的siRNAs,通常能够保证目的基因被有效地抑制。
dsRNA消化法的主要优点在于可以跳过检测和筛选有效siRNA序列的步骤,为研究人员节省时间和金钱(注意:通常用RNAse III通常比用Dicer要便宜)。不过这种方法的缺点也很明显,就是有可能引发非特异的基因沉默,特别是同源或者是密切相关的基因。现在多数的研究显示这种情况通常不会造成影响。
最适用于:快速而经济地研究某个基因功能缺失的表型
不适用于:长时间的研究项目,或者是需要一个特定的siRNA进行研究,特别是基因治疗
体内表达
前面的3种方法主要都是体外制备siRNAs,并且需要专门的RNA转染试剂将siRNAs转到细胞内。而采用siRNA表达载体和基于PCR的表达框架则属于:从转染到细胞的DNA模版中在体内转录得到siRNAs。这两种方法的优点在于不需要直接操作RNA。
4. siRNA表达载体
多数的siRNA表达载体依赖三种RNA聚合酶III 启动子(pol III)中的一种,操纵一段小的发夹RNA(short hairpin RNA, shRNA)在哺乳动物细胞中的表达。这三类启动子包括大家熟悉的人源和鼠源的U6启动子和人H1启动子。之所以采用RNA pol III启动子是由于它可以在哺乳动物细胞中表达更多的小分子RNA,而且它是通过添加一串(3到6个)U来终止转录的。要使用这类载体,需要订购2段编码短发夹RNA序列的DNA单链,退火,克隆到相应载体的pol III 启动子下游。由于涉及到克隆,这个过程需要几周甚至数月的时间,同时也需要经过测序以保证克隆的序列是正确的。
siRNA表达载体的优点在于可以进行较长期研究——带有抗生素标记的载体可以在细胞中持续抑制靶基因的表达,持续数星期甚至更久。
病毒载体也可用于siRNA表达,其优势在于可以直接高效率感染细胞进行基因沉默的研究,避免由于质粒转染效率低而带来的种种不便,而且转染效果更加稳定。
最适用于:已知一个有效的siRNA序列,需要维持较长时间的基因沉默。
不适用于:筛选siRNA序列(其实主要是指需要多个克隆和测序等较为费时、繁琐的工作)。
5. siRNA表达框架
siRNA表达框架(siRNA expression cassettes,SECs)是一种由PCR得到的siRNA表达模版,包括一个RNA pol III启动子,一段发夹结构siRNA,一个RNA pol III终止位点,能够直接导入细胞进行表达而无需事前克隆到载体中。和siRNA表达载体不同的是,SECs不需要载体克隆、测序等颇为费时的步骤,可以直接由PCR得到,不用一天的时间。因此,SECs成为筛选siRNA的最有效工具,甚至可以用来筛选在特定的研究体系中启动子和siRNA的最适搭配。如果在PCR两端添加酶切位点,那么通过SECs筛选出的最有效的siRNA后,可以直接克隆到载体中构建siRNA表达载体。构建好的载体可以用于稳定表达siRNA和长效抑制的研究。
这个方法的主要缺点是①PCR产物很难转染到细胞中(晶赛公司的Protocol可以解决这一问题)②不能进行序列测定,PCR和DNA合成时可能差生的误读不能被发现导致结果不理想。
最适用于:筛选siRNA序列,在克隆到载体前筛选最佳启动子
不适用于:长期抑制研究。(如果克隆到载体后就可以了)
(三)siRNA的转染
将制备好的siRNA,siRNA表达载体或表达框架转导至真核细胞中的方法主要有以下几种:
1.磷酸钙共沉淀
将氯化钙,RNA(或DNA)和磷酸缓冲液混合,沉淀形成包含DNA且极小的不溶的磷酸钙颗粒。磷酸钙-DNA复合物粘附到细胞膜并通过胞饮进入目的细胞的细胞质。沉淀物的大小和质量对于磷酸钙转染的成功至关重要。在实验中使用的每种试剂都必须小心校准,保证质量,因为甚至偏离最优条件十分之一个pH都会导致磷酸钙转染的失败。
2.电穿孔法
电穿孔通过将细胞暴露在短暂的高场强电脉冲中转导分子。将细胞悬浮液置于电场中会诱导沿细胞膜的电压差异,据认为这种电压差异会导致细胞膜暂时穿孔。电脉冲和场强的优化对于成功的转染非常重要,因为过高的场强和过长的电脉冲时间会不可逆地伤害细胞膜而裂解细胞。一般,成功的电穿孔过程都伴随高水平(50%或更高)的毒性。
3.DEAE-葡聚糖和polybrene
带正电的DEAE-葡聚糖或polybrene多聚体复合物和带负电的DNA分子使得DNA可以结合在细胞表面。通过使用DMSO或甘油获得的渗透休克将DNA复合体导入。两种试剂都已成功用于转染。DEAE-葡聚糖仅限于瞬时转染。
4.机械法
转染技术也包括使用机械的方法,比如显微注射和基因枪(biolistic particle)。显微注射使用一根细针头将DNA,RNA或蛋白直接转入细胞质或细胞核。基因枪使用高压microprojectile将大分子导入细胞。
5.阳离子脂质体试剂
在优化条件下将阳离子脂质体试剂加入水中时,其可以形成微小的(平均大小约100-400nm)单层脂质体。这些脂质体带正电,可以靠静电作用结合到DNA的磷酸骨架上以及带负电的细胞膜表面。因此使用阳离子脂质体转染的原理与以前利用中性脂质体转染的原理不同。使用阳离子脂质体试剂,DNA并没有预先包埋在脂质体中,而是带负电的DNA自动结合到带正电的脂质体上,形成DNA-阳离子脂质体复合物。据称,一个约5kb的质粒会结合2-4个脂质体。被俘获的DNA就会被导入培养的细胞。现存对DNA转导原理的证据来源于内吞体和溶酶体。
为了达到高的转染效率,在转染实验过程中,需要注意以下几点:
1.纯化siRNA
在转染前要确认siRNA的大小和纯度。为得到高纯度的siRNA,推荐用玻璃纤维结合,洗脱或通过15-20%丙烯酰胺胶除去反应中多余的核苷酸,小的寡核苷酸,蛋白和盐离子。注意:化学合成的RNA通常需要跑胶电泳纯化(即PAGE胶纯化)。
2.避免RNA酶污染
微量的RNA酶将导致siRNA实验失败。由于实验环境中RNA酶普遍存在,如皮肤,头发,所有徒手接触过的物品或暴露在空气中的物品等,此保证实验每个步骤不受RNA酶污染非常重要。
3.健康的细胞培养物和严格的操作确保转染的重复性
通常,健康的细胞转染效率较高。此外,较低的传代数能确保每次实验所用细胞的稳定性。为了优化实验,推荐用50代以下的转染细胞,否则细胞转染效率会随时间明显下降。
4.避免使用抗生素
Ambion公司推荐从细胞种植到转染后72小时期间避免使用抗生素。抗生素会在穿透的细胞中积累毒素。有些细胞和转染试剂在siRNA转染时需要无血清的条件。这种情况下,可同时用正常培养基和无血清培养基做对比实验,以得到最佳转染效果。
5.选择合适的转染试剂
针对siRNA制备方法以及靶细胞类型的不同,选择好的转染试剂和优化的操作对siRNA实验的成功至关重要。
6.通过合适的阳性对照优化转染和检测条件
对大多数细胞,看家基因是较好的阳性对照。将不同浓度的阳性对照的siRNA转入靶细胞(同样适合实验靶siRNA),转染48小时后统计对照蛋白或mRNA相对于未转染细胞的降低水平。过多的siRNA将导致细胞毒性以至死亡。
7.通过标记siRNA来优化实验
荧光标记的siRNA能用来分析siRNA稳定性和转染效率。标记的siRNA还可用作siRNA胞内定位及双标记实验(配合标记抗体)来追踪转染过程中导入了siRNA的细胞,将转染与靶蛋白表达的下调结合起来。
三、RNAi的应用前景
1. 研究基因功能的新工具
已有研究表明RNAi能够在哺乳动物中灭活或降低特异性基因的表达,制作多种表型,而且抑制基因表达的时间可以随意控制在发育的任何阶段,产生类似基因敲除的效应。线虫和果蝇的全部基因组序列已测试完毕,发现大量未知功能的新基因,RNAi将大大促进对这些新基因功能的研究。与传统的基因敲除技术相比,这一技术具有投入少,周期短,操作简单等优势,近来RNAi成功用于构建转基因动物模型的报道日益增多,标志着RNAi将成为研究基因功能不可或缺的工具。
2. 研究信号传导通路的新途径
联合利用传统的缺失突变技术和RNAi技术可以很容易地确定复杂的信号传导途径中不同基因的上下游关系,Clemensy等应用RNAi研究了果蝇细胞系中胰岛素信息传导途径,取得了与已知胰岛素信息传导通路完全一致的结果,在此基础上分析了DSH3PX1与DACK之间的关系, 证实了DACK是位于DSH3PX1磷酸化的上游激酶. RNAi技术较传统的转染实验简单、快速、重复性好,克服了转
染实验中重组蛋白特异性聚集和转染效率不高的缺点, 因此认为RNAi技术将可能成为研究细胞信号传导通路的新途径。
3.开展基因治疗的新策略
RNAi具有抵抗病毒入侵,抑制转座子活动,防止自私基因序列过量增殖等作用,因此可以利用RNAi现象产生抗病毒的植物和动物,并可利用不同病毒转录序列中高度同源区段相应的dsRNA抵抗多种病毒。
肿瘤是多个基因相互作用的基因网络调控的结果,传统技术诱发的单一癌基因的阻断不可能完全抑制或逆转肿瘤的生长, 而RNAi可以利用同一基因家族的多个基因具有一段同源性很高的保守序列这一特性, 设计针对这一区段序列的dsRNA分子,只注射一种dsRNA即可以产生多个基因同时剔除的表现,也可以同时注射多种dsRNA而将多个序列不相关的基因同时剔除。
尽管目前RNAi技术在哺乳动物中的应用还处于探索阶段,但它在斑马鱼和老鼠等脊椎动物中的成功应用预示着RNAi将成为基因治疗中重要的组成部分,人工合成的dsRNA寡聚药物的开发将可能成为极具发展前途的新兴产业。